세계 최초로 예전에 비해 최대 규모로 한국인 대장암 환자 3차원 게놈 지도 작성에 성공했습니다.
KAIST 생명과학과 정인경 교수 연구팀이 서울대학교 암연구소 김태유 교수 연구팀과의 공동연구를 통해 인공지능 기반 알고리즘을 활용, 한국인 대장암 환자의 3차원 게놈[1] 지도를 최초로 제시했는데요. 이를 토대로 암 세포 특이적인 유전자 조절 기전을 통해 특정 종양유전자들이 과발현되는 현상을 규명했다고 24일 밝혔습니다.
1차원적 게놈 서열 분석에 기반한 현재의 암 유전체 연구는 종양유전자들의 과발현 기작을 설명하는데 한계가 있었습니다. 하지만 3차원 공간상에 게놈이 어떻게 배열되는지를 분석하는 3차원 게놈 (3D genome) 구조 연구는 이러한 한계를 극복 가능하게 하는데요. 이번 연구에서는 정상 세포에서는 존재하지 않는 암 세포 특이적 염색질 고리(chromatin loop) 구조가 유전자 발현 촉진 인자인 인핸서와 종양유전자 사이의 상호작용을 형성하여 과발현을 유도하는 인핸서 납치(enhancer-hijacking)[2] 현상에 초점을 두어 연구했습니다.
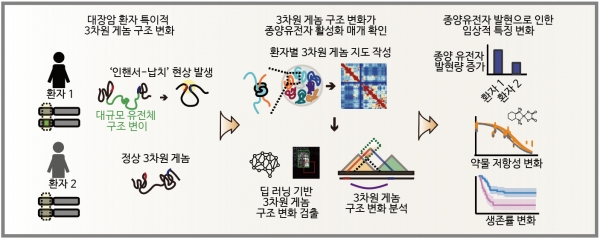
KAIST 생명과학과 김규광 박사과정이 주도한 이번 연구는 게놈간의 공간상 상호작용을 측정할 수 있는 대용량 염색체 구조 포착 Hi-C (High-throughput Chromosome Conformation Capture)[3] 실험 기법을 활용하여 대장암 3차원 게놈 지도를 만들었습니다. 그리고, 대장암 특이적 3차원 게놈 변화를 환자 개개인별로 분석할 수 있는 인공지능 기반 알고리즘을 개발했습니다. 그 결과 공동연구팀은 광범위한 규모의 3차원 게놈 구조 변화와 이로 인한 다양한 종양유전자의 활성화를 확인 할 수 있었습니다.
연구팀은 이번 연구를 통해 암 특이적 3차원 게놈 구조의 변화로 인한 종양유전자 활성 기작을 명확히 제시하였으며 이로 인한 환자 예후와 약물 반응 등 임상적인 특성과의 연관성까지 제시해 맞춤 치료 원천기술 확보에 기여했습니다.
지금까지 암 세포주에 대한 3차원 게놈 구조 연구는 일부 보고 되었으나, 대규모 환자 암조직에 대한 연구는 조직 내 세포 이질성, 종양 순도, 암세포 이질성[4] 등의 문제로 인한 정밀 암 특이적 3차원 게놈 구조 분석의 한계로 수행되지 못하였다.

반면에 이번 연구에서 연구팀은 AI 기반 알고리즘으로 환자 개인 종양 조직으로부터 얻어진 복잡한 신호를 해석할 수 있었는데요. 그 결과 최대 규모인 환자 40명의 종양 조직과 인접한 정상 대장 조직을 사용해 3차원 게놈 지도를 작성 가능했습니다. 또한 DNA 서열정보를 보여주는 전장유전체 지도의 경우 다양한 인종에 대해 생산되고 있고 한국인의 전장유전체 지도 또한 개발되었습니다. 한국인 3차원 게놈 지도, 특히 종양 조직에 대한 3차원 게놈 지도는 이번 연구에서 최초로 제시될 수 있었습니다.
서울대학교병원 혈액종양내과 김태유 교수는 “이러한 결과는 개별 암 환자들마다 서로 다르게 나타나는 종양 이질성을 이해하는 데 매우 중요한 요소가 될 수 있으며, 이를 이용한 환자 맞춤형 치료 연구의 시발점이 될 것이다”라고 말했습니다. KAIST 생명과학과 정인경 교수는 “기존의 점돌연변이나 유전체 변이만으로는 설명이 어려운 암 유전체를 3차원 게놈 구조 관점에서 재해독하고 신규 암 타겟을 발굴할 수 있는 수 있는 새로운 접근법을 제시했다”라고 밝혔습니다.
연구 결과는 국제 학술지, `셀 리포츠(Cell Reports)'에 7월 13일 자로 출판됐습니다.
논문명: Spatial and clonality-resolved 3D cancer genome alterations reveal enhancer-hijacking as a potential prognostic marker for colorectal cancer
#용어설명
1. 3차원 게놈
3차원 게놈은 세포핵 내 게놈이 핵 내부 공간에서 형성하고 있는 여러 계층의 구조들을 의미한다. 최근 핵 내 게놈이 핵 안에 무작위로 배치되는 것이 아닌 특정한 구조를 이루며 존재한다는 사실들이 밝혀지고 있으며 이러한 구조들은 정확한 유전자 발현 조절에 중요한 역할을 하는 것으로 알려져 있다.
2. 인핸서 납치
인핸서 납치 (enhancer-hijacking) 은 정상적인 인핸서 (enhancer)–프로모터 (promoter) 간의 상호작용이 3차원 게놈의 (비정상적인) 변화로 인해 잘못된 인핸서-프로모터 상호작용의 발생을 의미한다. 잠재적 종양유전자(proto-oncogene) 의 발현에 영향을 주는 것으로 보고되었으며 이전까지 기전이 불분명한 비전사 지역에 위치한 유전체 구조변화의 기능을 해독할 수 있는 주요 기전으로 예상된다.
3. Hi-C
게놈 3차구조를 분석하는 차세대염기서열분석법 기반의 실험 방법으로 멀리 떨어져있는 게놈 지역간의 공간상의 상호작용을 측정한다. 본 실험 기법을 적용하며 전 게놈간의 공간상의 상호작용을 측정해 염색질 고리 (chromatin loop) 등의 현상을 관찰할 수 있다.
4. 암의 클론성/종양이질성
암의 클론성(clonality) 혹은 종양이질성(tumor heterogeneity) 는 암이 악성 변이를 겪은 전구세포로부터 분화한다는 것을 의미한다. 이러한 클론들이 주변 환경에 의한 진화(clonal evolution)를 겪으며 다른 형태의 유전적 변이들을 축적하여 유전적으로 다양한 종양 조직이 형성된다. 역으로 다수의 클론들에서 변이들이 나타나는 빈도를 비교 분석함으로서 주요 변이들의 발생 시점과 빈도를 추적할 수 있다.

